💡
原文中文,约4700字,阅读约需12分钟。
📝
内容提要
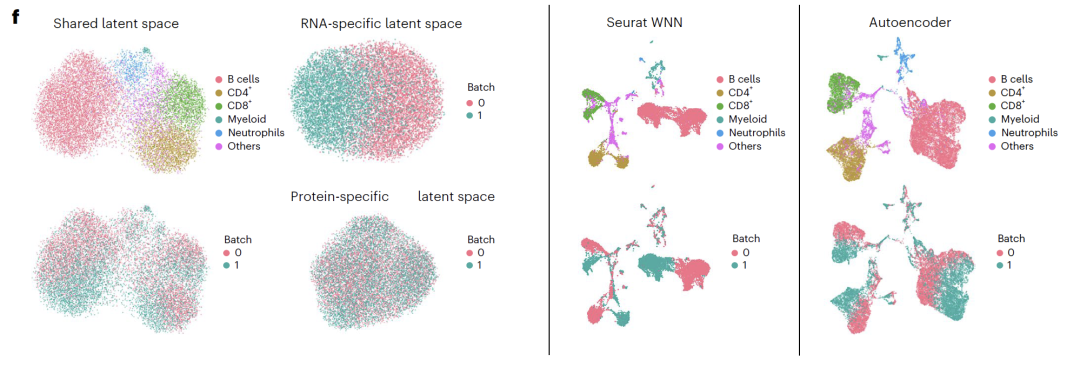
麻省理工学院与苏黎世联邦理工学院提出的APOLLO框架,解决了单细胞生物学中多模态数据整合的挑战,能够有效解耦共享信息与模态特异性信息,从而提高细胞状态解析的精度。该框架利用深度学习,推动单细胞技术在疾病机制研究中的应用。
🎯
关键要点
- 麻省理工学院与苏黎世联邦理工学院提出APOLLO框架,解决单细胞生物学中多模态数据整合的挑战。
- APOLLO框架能够有效解耦共享信息与模态特异性信息,提高细胞状态解析的精度。
- 该框架利用深度学习,推动单细胞技术在疾病机制研究中的应用。
- 当前分析方法存在显著局限,难以捕捉模态间的深层关联。
- APOLLO通过显式建模共享信息和模态特异性信息,为解析细胞状态提供技术路径。
- 研究成果已发表于Nature Computational Science,题为《Partially shared multi-modal embedding learns holistic representation of cell state》。
- APOLLO框架采用两步训练策略,学习部分重叠的潜在空间,有效识别多种模态间的生物学信号。
- 研究使用多个公开的多模态单细胞数据集评估APOLLO的性能,包括测序与成像数据。
- APOLLO能够揭示蛋白亚细胞定位差异与细胞区室形态之间的关联。
- APOLLO模型通过潜在优化策略,自动学习并解耦多模态中的共享信息与特有信息。
- APOLLO在配对测序数据整合、跨模态预测等方面表现出独特优势。
- 全球学术界对单细胞多模态数据整合技术的关注日益增加,推动精准医疗的发展。
- BioNTech公司将单细胞多模态数据整合技术应用于肿瘤免疫治疗与个性化疫苗研发。
➡️


